
16
Raquel Camacho-Luque
Detección de carbapenemasas en pseudomonas aeruginosa
INTRODUCCIÓN
Pseudomonas aeruginosa
presenta con frecuencia resisten-
cia a múltiples antibióticos incluyendo carbapenemes, así como
una elevada capacidad para adquirir nuevas formas de resisten-
cia, bien por mutaciones o mediante la adquisición de nuevos
genes (1-2). La resistencia a carbapanemes se ha incrementado
en los últimos años causada por diferentes mecanismos, los más
frecuentes son la sobreexpresión de bombas de expulsión y el
cierre de porinas OprD (3), aunque no son los únicos ya que en la
actualidad la aparición de enzimas que pueden hidrolizar carba-
penemes está cobrando cada vez más importancia.
Las carbapenemasas son enzimas que hidrolizan el grupo
amida del anillo betalactámico. Según la clasificación de Ambler
se pueden estructurar en tres grupos: clase A (grupo 2f de Bush-
Jacoby-Medeiros, dependientes de serina e inhibidas parcialmen-
te por el ácido clavulánico, inducibles, no trasferibles; clase B
(grupo 3 de Bush-Jacoby-Medeiros), dependientes de zinc, inhi-
bidas por EDTA, inducibles o asociadas a plásmidos conjugativos;
y clase C, oxacilinasas.
La espectrometría de masas MALDI-TOF MS ha sido introdu-
cida en la rutina de trabajo de los laboratorios de microbiología
para la identificación de bacterias y hongos, y puede constituir
una herramienta útil en complejos procesos diagnósticos (4). La
detección de carbapenemasas por MALDI-TOF MS es un méto-
do directo de identificación no estandarizado en la rutina de los
laboratorios, que está basado en el análisis espectrofotométrico
de la degradación del meropenem por una cepa productora de
carbapenemasa (5-6). Los datos que avalan su utilización para el
diagnóstico rápido de carbapanemasas en aislados clínicos, o a
partir de frascos de hemocultivo positivos en los que se identifica
Ps. aeruginosa
mediante MALDI-TOF MS son muy escasos.
MATERIAL Y MÉTODOS
Hemos utilizado cultivos en placa (agar sangre Columbia 5%)
de 45 aislados clínicos de
Ps. aeruginosa
con diferente sensibili-
dad a carbapenemes, 25 sensibles a meropenem y 20 resistentes
(clasificados fenotípicamente mediante sistemas automatizados
Wider, Vitek). Dentro del grupo de cepas resistentes a carbapene-
mes hemos empleado 18 cepas productoras de carbapenemasa A
y/o B; y 8 cepas con impermeabilidad de membrana, determina-
do dichos mecanismos de resistencia mediante método de difu-
sión disco-placa, utilizando meropenem 10µg, meropenem 10µg
+ ácido borónico, meropenem 10µg + cloxacilina y meropenem
10µg + ácido dipicolínico (Rosco Diagnostica), combinaciones
cuya interpretación permite establecer si la cepa es productora
de carbapenemasa clase A o si es productora de carbapenemasa
clase B (7).
Para determinar la presencia de carbapenemasa mediante
el análisis por espectrometría de masas MALDI-TOF MS (Bruker
Daltonics GmbH, Bremen, Germany) se utilizó cultivo de
Ps. aeru-
ginosa
y se incubó a 37ºC durante 3 horas y media junto a 10µl de
meropenem (AztraZeneca, 10 mg/ml H2O HPLC) en tubos eppen-
dorff estériles. Tas centrifugar el eppendorf durante 2 minutos a
16000rpm, se depositó 1µl del sobrenadante en la placa del es-
pectrómetro de masas MALDI-TOF MS añadiendo tras secado 1µl
de matriz HCCA (Ácido -cyano-4-hidroxicinámico). Los espec-
tros se obtuvieron en el rango de masas de 100-1000 Da usando
una intensidad de láser 25-35%, cada espectro era la suma de 240
disparos por láser.
Los espectros adquiridos por MALDI-TOF MS se analizaron
mediante el software Flexanalysis 3.3 (Bruker Daltonics GmbH,
Bremen, Germany) usando el protocolo descrito por Sparbier
et al (8). En primer lugar el espectro es suavizado (algoritmo Sa-
vitzkyGolay, amplitud 0.2 m/z, ciclo) y posteriormente el espectro
se ha adaptado a la línea base (algoritmo, TopHat). Los picos son
automáticamente seleccionados con el ajuste de los siguientes
parámetros: algoritmo de detección de picos: centrado; máxima
señal de detección :2; mínimo umbral de detección 0% ; umbral
de intensidad relativa 0%; altura 80%; y son comparados con
la masa molecular del meropenem junto a un átomo de hidró-
geno [M+H] (384.5 Da) y en forma de sales [M+Na] (406.5 Da),
[M+2Na] (428.5 Da) con una tolerancia de 0.5 m/z.
Todos los ensayos se calibraron de a cuerdo a lo descrito por
Sparbier et al (8). La calibración se realizo previa a la determina-
ción de los espectros. Para ello se utilizó un calibrador externo
suministrado por Bruker Daltonics (GmbH, Bremen, Germany),
ajustando los valores de cuatro compuestos bien identificados
a su respectivo valor m/z conocido. Dos de estos picos corres-
ponden a la matriz HCCA (alto 379.09 m/z y bajo 190.44 m/z) y
otros dos a la bradiquinina 1-5 (572.76 m/z) y a la bradiquinina
1-7 (756.85 m/z).
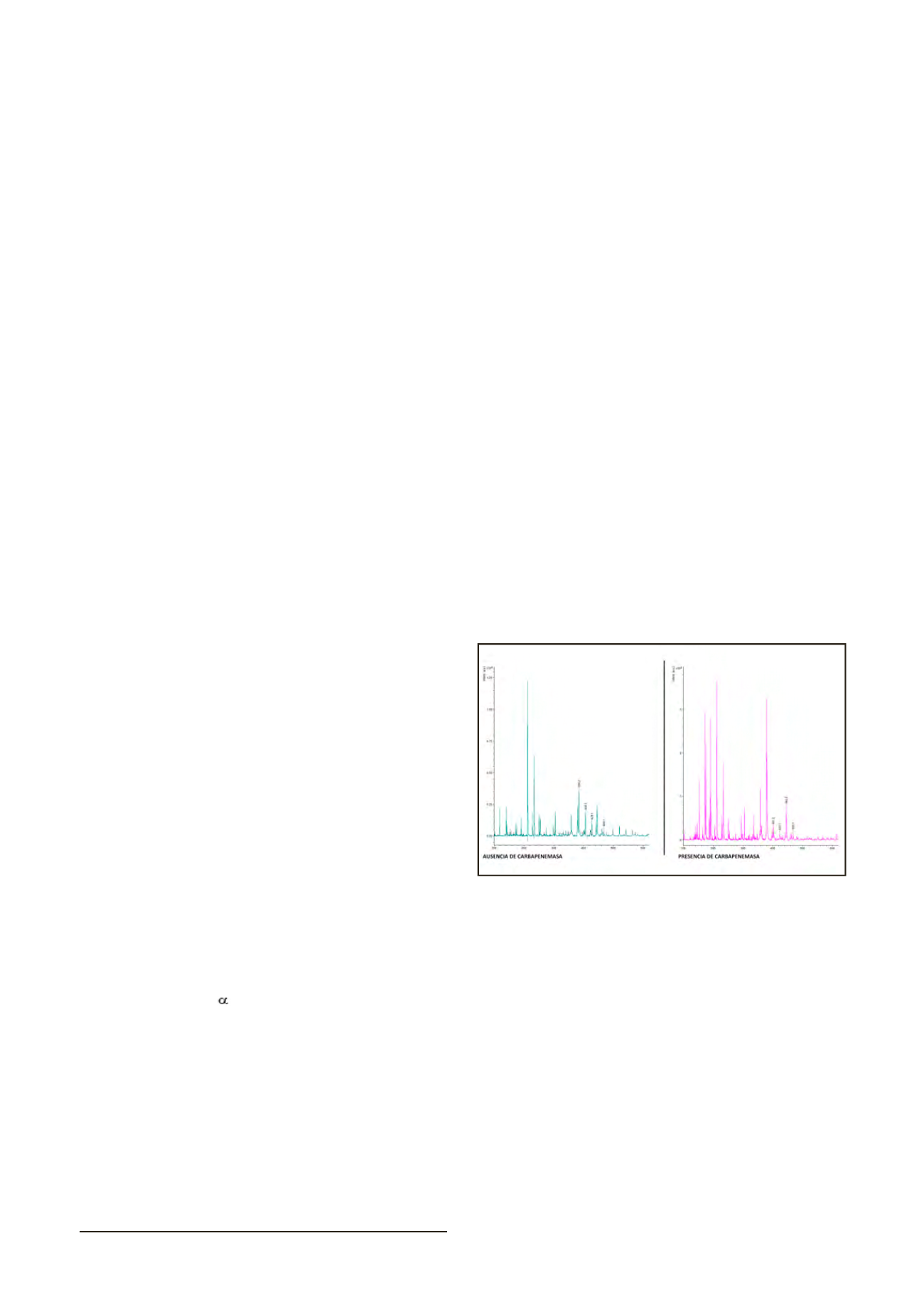
RESULTADOS
Si la cepa de
Ps. aeruginosa
es productora de carbapene-
masa se produce la hidrólisis del anillo betalactámico del me-
ropenem, modificándose así el pico correspondiente a la masa
molecular original del meropenem (+ 18 Da). Tanto la molécula
de meropenem original (383.5 Da) como su forma hidrolizada
(401.5 Da), meropenem resistente por presencia de carbapene-
masa, pueden detectarse en distintas formas de ionización por el
espectrómetro de masas. En ausencia de carbapenemasa los pi-
cos detectados son los correspondientes a la masa molecular del
meropenem junto a un átomo de hidrógeno (H): 384.5 Da [M+H],
la adición de 1átomo de sodio (Na): 406.5 Da [M+Na] y 2 átomos
de sodio (2Na): 428.5 Da [M+2Na]. En el caso de la hidrólisis del
meropenem por la presencia de carbapenemasa se obtiene el
pico 401.1 Da junto a sales de sodio, que corresponderían a los
picos 423.2 Da (Na), 445.0 Da (2 Na) y 468.1 Da (3 Na). (Figura 1)
De las 12 cepas productoras de carbapenemasas clase A o B,
(2/12 clase A, 10/12 clase B) la técnica de espectrometría de ma-
sas MALDI-TOF MS detectó picos de degradación del antibiótico
en estudio correspondientes a la presencia de carbapenemasas
en 11/12 casos (94.4%). Tan solo una cepa clasificada por la téc-
nica de difusión disco-placa como productora de carbapenema-
sa clase A no fue detectada por la técnica de espectrometría de
masas MALDI-TOF. Esta cepa fue clasificada como productora de
carbapenemasa clase B mediante técnicas moleculares de PCR.
En las cepas usadas como controles negativos, la espectro-
metría de masas MALDI-TOF indicó la ausencia de carbapenema-
sas clase A o B en 31/33 (93.9%) casos En un caso se encontraron
picos de degradación por MALDI-TOF MS® y en el otro caso se
obtuvo un espectro con mezcla de picos del meropenem intacto
e hidrolizado. Mediante técnicas moleculares de PCR estas cepas
se clasificaron respectivamente como cepa no productora de car-
bapenemasa y cepa productora de carbapenemasa clase B (IMP).
Figura 1. Espectro lectura MALDI-TOF-MS

















